介绍一个综合 chip-seq,RNA-seq 综合性预测转录调控网络的数据库:
GRAND: https://grand.networkmedicine.org/
背景数据集
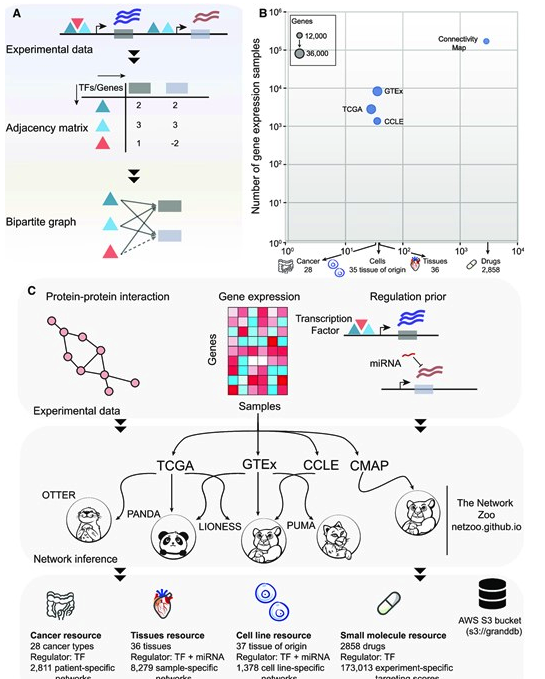
由于是要分析转录调控对于基因的影响,所以作者首先收录了对于 Gene/TF/miRNA 和基因靶基因的关系。关于这个部分的数据主要来自于这篇文献:Gene targeting in disease networks: https://arxiv.org/abs/2101.03985

同时除了基本的靶向关系也需要知道知道具体的表达关系。另外对于小分子物质对于基因表达的影响,作者也纳入了 Connectivity Map 来进行分析。
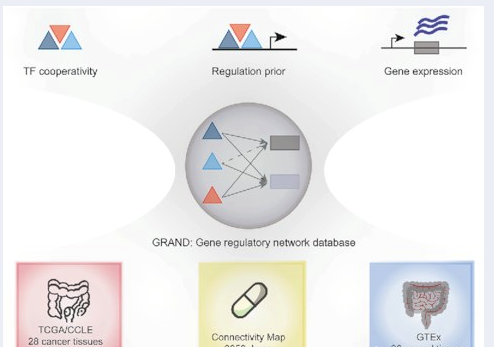
最后在得到这些数据之后,利用 PANDA 的算法来综合性分析基因转录调控的关系。
数据库使用
在 GRAND 当中主要包括了两个模块的功能:
1. 调控网络查询
在网络查询当中,我们可以看到基于不同的分析类型分成了,小分子物质,肿瘤,组织,细胞系四个调控网络分析数据库。这里,我们使用组织来进行说明。
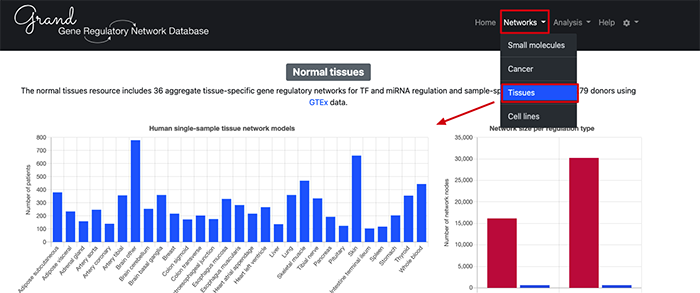
点击之后我们就可以看到具体的分析情况。下面有每一个组织的具体分析列表,里面除了基本的组织类型还有使用的分析方法。例如,我们想查看乳腺 的调控网络。
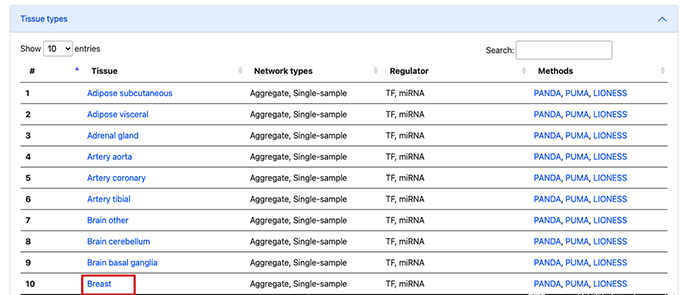
点击之后,在下方可以看到一个基于不同算法预测的不同的调控关系的表格。例如我们想看基于 PANDA 预测的 TF-Gene 的调控网络。
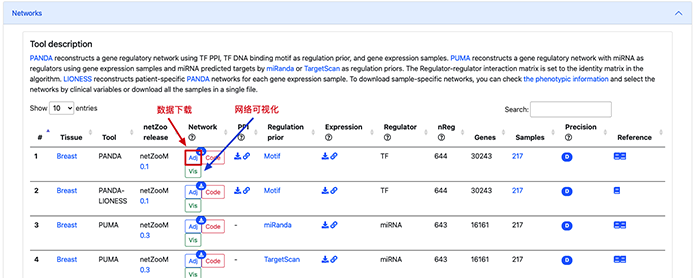
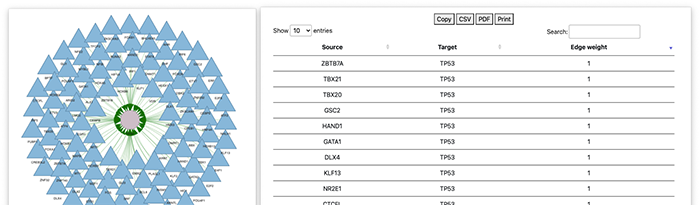
我们可以点击Vis来可视化调控网络。在调控网络当中,我们可以输入我们想要查找的基因的调控信息点击Submit就可以进行查找。例如,我们想要看TP53的调控网络。
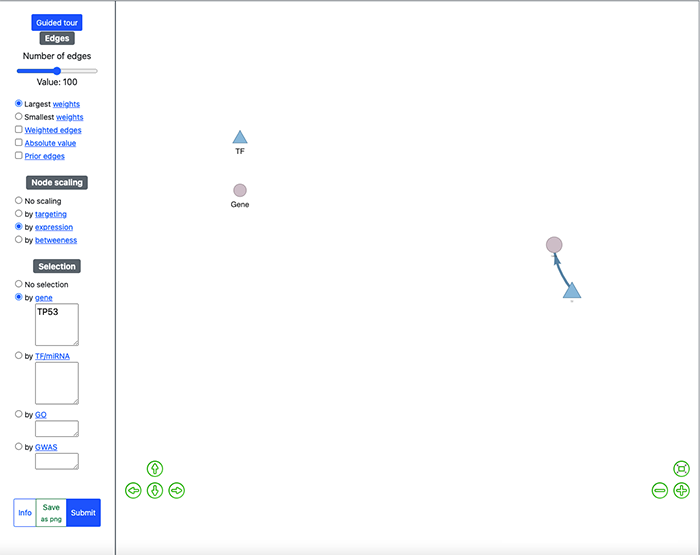
经过分析就可以得到 TP53 的调控网络了。同时也提供了数据下载的表格
2. 调控网络分析
在分析的部分,主要提供了两个主要的功能,一个是基于转录因子/基因来分析具体的药物作用靶点的功能
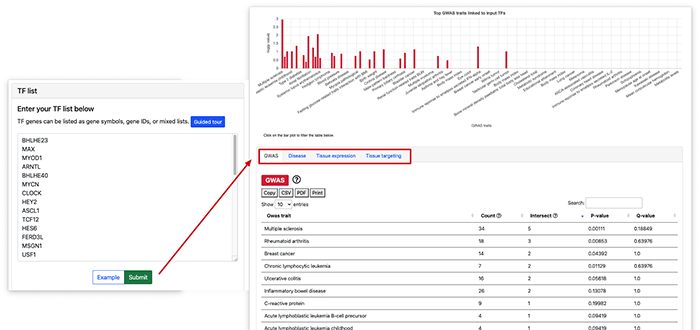
另外一个则是对转录因子进行富集分析的功能。不过这里转录因子的富集不是基于功能的富集,而是基于 GWAS, 疾病,组织表达和组织靶点的富集。
以上就是这个数据库的主要使用方法了。虽然没有提供所有数据下载的功能。但是对于分析的某一个具体组织,作者还是提供了数据下载的地方了。基于简单的靶点+表达数据的调控网络预测和普通的靶点预测比起来相对来说要准确一些。所以有需要预测相对于转录调控靶点的,可以尝试一下这个数据库哈。
另外如果想要自己分析一些转录调控的话,作者所有的分析算法都是基于 ZOO 的一个算法来的。具体可见:The network zoo
The network zoo: https://netzoo.github.io/